行政院國家科學委員會補助
大專學生參與專題研究計畫研究成果報告
*************************************
計畫: 利用Y染色體上PPr-Y與ORY基因的遺傳變異
名稱:
研究隱蔽種階段黃果蠅之族群遷移
*************************************
執行計畫學生:秦安侖
學生計畫編號:NSC 91 -2815-C-001- 011
-B
研
究 期 間 :九十一年七月一日至九十二年二月底止,計八個月
指
導 教 授 :曹順成
研究動機與問題
1993年Begun和Aquadro發現從Zimbabwe採集的黃果蠅(Drosophila melanogaster)與北美地區的黃果蠅在DNA層次上有很大的差異;Wu et al. (1995)隨後研究發現Zimbabwe採集的D. melanogaster與鄰近地區的同種果蠅有明顯的單向生殖隔離(sexual isolation);研究指出,即使為同種,別處採集的雄性果蠅,不會與在Zimbabwe採集的雌性果蠅交配。
一向以來,我們一直認為物種分化的演化模型,通常是藉由地理隔離來造成同種族群間基因變異的累積,當累積到一定的程度時,該種處於兩地的族群便會產生生殖隔離,從而達到我們一般定義的新物種形成。但是這個模型的證明,卻面臨一個很大的問題:基因變異的累積過程,許多的事件或動態上的資訊,會在種化完成後在基因資料中被遺失掉;而這也造成在已經形成的物種間研究種化的分子演化時一個很大的障礙,從而科學家開始試圖以這個模型去定義處於「種化階段的物種(incipient speciation)」與尋找這樣狀態的物種,作為研究的材料。根據這樣的定義,生殖隔離的形成,代表雙方的遺傳物資無法經由交配而混和,以及流通到雙方各自的族群基因庫(gene pool)中;因此,不是雙方的個體間無法交配或生育下一代,就是雙方雜交後產生的下一代沒有生育能力(sterile)。
由於黃果蠅是一種分布廣泛的類種,與其他果蠅種間的生殖隔離非常完全。Zimbabwe發現的黃果蠅咸被相信正處於從該物種分化出新種的階段中,且由後續的許多研究指出分子層次的生殖隔離佔重要的地位(Hollocher et al., 1997)。由於這個研究也間接的支持雌性選配的生殖隔離理論(female choice of sexual isolation),因此後續的研究也著重在兩地的黃果蠅間的體染色體與X染色體上,並已經發現了染色體層次上不少的決定區域,有利於發現此種分化的決定基因、乃至於果蠅性行為基因層次研究的突破(Ting et al., 2001)。不過Johnson and Palopoli研究指出Y 染色體並沒有在這生殖隔離中扮演重要的地位。
果蠅的Y染色體,因為其染色體結構的關係,本身就具有基因研究上的困難。研究指出在果蠅,不同於哺乳動物,決定性別的基因並不是在Y 染色體上;但是Y 染色體上仍然被證明其存在與否決定了雄性果蠅的生殖力(Bridges 1916),並且也有新近發現相關的基因提供證據(Gepner and Hays, 1993)。
|
fig. 1. 圖示黃果蠅在北美品種與Zimbabwe品種的生殖隔離。 |
由於兩地的黃果蠅之間,生殖隔離並不是非常的完全,所以兩者之間的基因仍然有互相流通的可能性。不過,即使在Y染色體上面,應該並沒有對這個新種分化有重要影響的基因存在,由於Y染色體並不容易與X染色體等其他染色體互換,我們做了一個假設:在Zimbabwe與其他地方採集的黃果蠅,Y染色體上的遺傳變異會比較容易累積,而不 |
會在雜交時的基因流動中互相交換而稀釋掉了彼此的變異差異。由於果蠅Y 染色體上有大量的異染色質(heterochromatins),有意義的序列變異研究必須在基因上著手。A. B. Carvalho和A. G. Clark的團隊,在2000與2001年時,運用新的想法與技術,在果蠅的Y 染色體上發現了因許多過去技術上的瓶頸而無法定位的九個蛋白質基因(protein coding gene)。我們計劃選取新近發現在Y染色體上的PPr-Y與ORY兩個基因(Calvalho et al., 2001)的序列比對,來研究Zimbabwe和其他地區黃果蠅族群間的基因變異。
PPr-Y(protein phosphatase 1 regulatory subunit)經Carvalho的研究,發現其為大約1.7kb大小的基因;RT-PCR的定序則是約1.2kb的exon。不過此一exon卻在alternative splicing中會有兩種產物,分別是較小(223 residues)與較大(569 residues)的兩個蛋白質;序列分析證明整段exon的前端、構成較小蛋白質的部分,相似於酵母菌的Sds22p基因。兩者主要都發現有leucine-rich repeat。Sds22p已經證實是dynein light chain的一部分,有關於dynein light chain的一些signal transduction pathways與其和heavy chain上motor domain結合的作用。PPr-Y的後段基因,Carcalho在序列分析上找不到與其有相似的基因或片段,不過並無法證實這一後段的基因、乃至於splicing後的較大蛋白質產物,是沒有功能性的。因此,我們準備將PPr-Y整段約1.2kb的基因都選取為研究比較的對象,並希望可能可以以此研究後段基因是否有功能性存在。
ORY(Occludin-related Y)是坐落在ks-1區域的基因,序列上充斥著coiled-coiled motifs,一般認為具有蛋白質間作用的一種功能區;也因此,序列比對上與ORY相似的基因很多,不容易藉由序列的對比推測其功能;Carcalho則發現了此一基因與老鼠的一個相關雄性生殖力的膜蛋白occludin/ELL domain與兩者蛋白質表現的相似性,因此認為ORY可能在功能上也與occludin有關。我們也希望可能可以從序列比對中,找出ORY基因結構上可能提供的演化與功能線索。
以此兩基因為基礎,配合其他現有在體染色體與X染色體上已知的基因序列,我們希望可以從黃果蠅與其Zimbabwe採集種,以及選取其他種的果蠅(D. simulans, D. mauritiana),作序列變異的研究,以觀察在種間、和處於生殖隔離的分種狀態下的果蠅間,在Y染色體、X 染色體或體染色體上,基因序列上突變保存程度和生殖隔離的關係,提供在演化時基因突變動態上的一些資訊與線索;以及基因結構上的額外比對,可能可以提供這些基因一些分子演化上功能的發現與進一步研究。
研究方法及步驟
A. 遺傳學研究
我們選定以下十個黃果蠅品系:Or-Rc作為尋常的品系,以及FR,兩者分別取自美洲與歐洲;ZH13、ZH29、ZH21、ZH32與ZS29、ZS 6、ZS30、ZS49兩組分別是採自不同地點的Zimbabwe黃果蠅品系,並各自由左到右有Zimbabwe品系果蠅如前述一般的交配行為從弱到強的程度排列(Fang, et al. 2002)。
我們取~5269 FM7d,w1 oc1 ptg1 / C(1)DX, y1 f1 初步與選取的十個品系進行雜交實驗:分別取各品系單隻雄果蠅與數隻~5269品系雌果蠅交配,並對其後代的雌雄比例進行計量。由於C(1)DX / 0 的雌性果蠅因為缺乏性染色體上的部分核醣體核醣核酸(rRNA)基因(bb)而無法生存,故此雜交實驗可以初步的偵測果蠅品系的Y染色體基因型。
B. 建立X與Y染色體單一來源的果蠅品系
我們選取每個品系的單隻雄果蠅,分別與~5269品系的處女雌果蠅及同品系的處女雌果蠅數隻交配,並分別採集前者後代的處女雌果蠅與後者的雄果蠅。如此則採集的兩邊所持有的Y染色體都來自同一隻雄果蠅,雜交之後的後代便可以建立品系保存,此品系中雄果蠅都會持有源自選取的單隻雄果蠅X及Y染色體。(fig. 2)我們可以用此一建立出的品系大量蒐集X與Y染色體進行定序的工作。
C. 分子生物實驗方法
我們採用PUREGENETM Genomic DNA Purification Kit提供的標準程序進行多果蠅的Genomic DNA萃取純化。經由自行設計的引子進行分段的PCR估計自EST data中預估在Y染色體中的intron大小與基因序列。PCR反應後的成品經過QIAquick Gel Extraction Kit處理後進行自動定序。
|
|
管/雄蟲 |
|
總數 |
♀/♂ |
|
|
管/雄蟲 |
總數 |
♀/♂ |
|
|
Or-Rc |
1 |
♂ |
57 |
0.81 |
|
FR 3V-1 |
1 |
♂ |
70 |
0.74 |
|
|
|
♀ |
46 |
|
|
|
|
♀ |
52 |
|
|
|
|
|
|
|
|
|
2 |
♂ |
81 |
0.75 |
|
|
|
|
|
|
|
|
|
♀ |
61 |
|
|
|
3 |
♂ |
79 |
0.76 |
|
|
|
|
|
|
|
|
|
♀ |
60 |
|
|
|
|
|
|
|
|
|
4 |
♂ |
110 |
0.96 |
|
|
4 |
♂ |
106 |
0.78 |
|
|
|
♀ |
106 |
|
|
|
|
♀ |
83 |
|
|
ZH13 |
1 |
♂ |
80 |
0.85 |
|
ZS29 |
1 |
♂ |
69 |
0.75 |
|
|
|
♀ |
68 |
|
|
|
|
♀ |
52 |
|
|
|
2 |
♂ |
81 |
0.7 |
|
|
2 |
♂ |
69 |
0.83 |
|
|
|
♀ |
57 |
|
|
|
|
♀ |
57 |
|
|
|
3 |
♂ |
65 |
0.69 |
|
|
3 |
♂ |
63 |
0.97 |
|
|
|
♀ |
45 |
|
|
|
|
♀ |
61 |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
ZH29 |
1 |
♂ |
114 |
0.91 |
|
ZS 6 |
1 |
♂ |
85 |
0.87 |
|
|
|
♀ |
104 |
|
|
|
|
♀ |
74 |
|
|
|
2 |
♂ |
74 |
1.07 |
|
|
2 |
♂ |
76 |
0.71 |
|
|
|
♀ |
79 |
|
|
|
|
♀ |
54 |
|
|
|
3 |
♂ |
79 |
0.78 |
|
|
3 |
♂ |
76 |
0.78 |
|
|
|
♀ |
62 |
|
|
|
|
♀ |
59 |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
ZH21 |
1 |
♂ |
73 |
0.84 |
|
ZS30 |
1 |
♂ |
61 |
0.87 |
|
|
|
♀ |
61 |
|
|
|
|
♀ |
53 |
|
|
|
2 |
♂ |
83 |
0.92 |
|
|
2 |
♂ |
69 |
0.67 |
|
|
|
♀ |
76 |
|
|
|
|
♀ |
46 |
|
|
|
3 |
♂ |
64 |
1.02 |
|
|
3 |
♂ |
68 |
0.97 |
|
|
|
♀ |
65 |
|
|
|
|
♀ |
66 |
|
|
|
|
|
|
|
|
|
|
|
|
|
|
ZH32 |
1 |
♂ |
69 |
1 |
|
ZS49 |
1 |
♂ |
83 |
0.69 |
|
|
|
♀ |
69 |
|
|
|
|
♀ |
57 |
|
|
|
2 |
♂ |
72 |
0.53 |
|
|
2 |
♂ |
78 |
0.64 |
|
|
|
♀ |
38 |
|
|
|
|
♀ |
50 |
|
|
|
3 |
♂ |
70 |
0.63 |
|
|
3 |
♂ |
56 |
0.55 |
|
|
|
♀ |
44 |
|
|
|
|
♀ |
31 |
|
表一 各品系雄果蠅與~5269雌果蠅雜交實驗結果
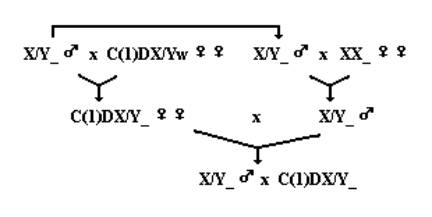
fig. 2 圖示定序用單一來源X與Y染色體果蠅品系建立方法
結果與討論
Ybb-是果蠅Y染色體以知最容易偵測的突變之一。Bb所決定的rRNA基因,將會直接的影響該果蠅體內蛋白質產生的速度;故在Y染色體上產生的Ybb-突變,若得不到X染色體上其他bb基因的補助,該果蠅便無法順利的生長。~5269持有的結合X染色體(compound X),在兩段X染色體結合的地方剛好缺失了彌補bb基因的重要片段,故伴隨著結合X染色體的Y染色體,勢必不能有Ybb-突變,才能保存其雌體的存活。藉由與~5269雜交的實驗結果,我們可以大致的推論所選取的十個品系中,含Ybb-突變基因的比例並不高。這是一個少數可以用遺傳學方法鑑定Y染色體基因型的基因突變;這個結果可以幫助我們確定建立單一來源X與Y染色體的品系所可以避免的障礙。
我們用Oligo 4、DNASTAR的PrimerSelect、以及Amplify 2.0程式進行引子設計與電腦模擬PCR結果。抽取基因體DNA直接進行Ppr-Y基因三段的PCR,皆無法抓到taq反應兩分鐘以內的產物,顯示Ppr-Y基因在Calvalho團隊以RT-PCR分析的結果內至少有兩到三個以上超過1kb的introns,而其中也包括了跨越Y染色體上E15 Kennison line的部分。在未能設計引子進行更詳細的分析之前,無法判定該基因的結構、E15 Kennison line與Ppr-Y蛋白質預測的兩種產物之間的關係。
ORY基因上,我們設計了四段的PCR引子對,初步分析出Or-Rc品系的基因體上,在EST資料庫裡被確定為ORY基因序列片段的AE002695與AE002654之間有約500bp大小的intron;而在AE003328與AE002695、AE002654與AE003352之間introns可能都大於2kb。
由於分別在RT-PCR與直接用基因體DNA進行PCR定序的工作遭遇不少待分析與解決的問題,完整的序列目前並無法成功的分析出。較值得討論的情形如下:
一、 在對引子對進行鑑定時,確定可以於FR品系在AE002695與AE002654之間夾到500bp大小產物的引子對,在Or-Rc品系上卻只能得到非常稀少的產物(fig.3(a))。可能的推測包括中間intron大小的極大差異,但較有可能的情形應是在引子預定沾粘的位置上序列的差異導致;這推測也可以由下面的一些討論再次支持。
二、 同一個引子對,在選取的十個品系上進行PCR的結果,產物的品質差異常常很大。我們遭遇到最明顯的例子:夾取ORY基因前段序列、AE003328上小段的55bp intron之前約500bp大小的引子對,在Or-Rc可以夾到正常產量與預期大小的產物,ZS30、ZS49與ZH21上也可以得到產量略小的產物,而同一條件下的反應在ZS 6、ZH13與ZH29上面則毫無產物(fig.3.(b))。在不預期中間有大片段的intron的前提下,合理的解釋便是在預定引子沾粘的序列上的變異所致。
|
|
fig.3.(a) 對FR’ ZH13’ ZH29’ ZS 6與Or-Rc品系基因體DNA進行PCR。由左到右分別是:Or-Rc、FR,用ORY1053+~1743-引子對;Or-Rc、FR,用ORY1053+~1215-引子對;1kb DNA ladder;FR、ZH13、ZH29、ZS 6,用ORY24+~480-引子對。 1053+到1215-剛好橫跨在AE002695與AE002654之間,故所夾到的DNA大小應可以判算此兩個EST序列之間的intron大小。 ORY24+~480-引子對,只能在FR與ZH13上夾出微弱的產物。這一結果經過兩次以上的檢驗。 |
|
|
|
fig.3.(b) 由左到右八個為一組,分別是各品系DNA:FR、ZH13、ZH29、ZS 6、ZS30、ZS49、Or-Rc、ZH21;中間間隔一個空槽,左右八組分別為:左邊是ORY24+~480-引子對,右邊為ORY1053+~1743-。 可以觀察到同一組引子對,在品系之間PCR的產物量有極大的差距。這一結果經過兩次以上的檢驗。 |
|
在還沒有完整的定序之前,我們尚無法針對所提出的演化問題進行解答與分析。但倘若以目前的結果而推論說在ORY基因、乃至Y染色體上的基因都有著顯著的品系間差異存在,一則是包括ORY基因在內的許多Y染色體基因都可能相關於雄果蠅的生殖能力,這種顯著的差異會否對基因表現後的功能有所影響還待商榷;二則是比較起來,在X染色體上又會否有同樣的差異度存在?我們建立的果蠅品系已經將雄果蠅的X與Y染色體都控制成為單一來源,故也可以用做X染色體定序的材料;除了可以選取X染色體上的基因進行各品系的定序與鑑定外,初步用來進行染色體的檢查工作、以夾X染色體上的引子對所做的PCR結果,暗示的差異也讓我們不得不質疑這一點(fig.4.)。
|
|
fig.4. 從左到右分別是品系FR、ZH13、ZH29、ZH32、ZS29、ZS 6、與Or-Rc,使用CO+~1134-引子對,夾X染色體上OdsH基因exon 1部位,預期產物大小為700bp。 |
參考文獻
1. Begun, D. and Aquadeo, C. F. (1993) African and North American populations of Drosophila melanogaster are very different at the DNA level. Nature (London) 365, 548-550
2. Wu, C.- I., Hollocher, H., Begun, D., Aquadeo, C. F.,Xu, I., and Wu, M. L. (1995) Sexual isolation in Drosophila melanogaster: A possible case of incipient speciation. Proc. Natl. Acad. Sci. USA 92, 2519-2523
3. Hollocher, H., Ting, C.-T., Wu, M. L., and Wu, C. I.(1997) Incipient speciation by sexual isolation in Drosophila melanogaster extensive genetic divergence without reinforcement. Genetics 147, 1191-1201
4. Hollocher, H., Ting, C.-T., Wu, M. L., and Wu, C. I(1997) Incipient speciation by sexual isolation in Drosophila melanogaster: variation in mating preference and correlation between sexes. Evolution 51, 1175-1181
5. Ting, C.-T., Takahashi, A., and Wu, C.-I. (2001) Incipient speciation by sexual isolation in Drosophilar: concurrent evolution at multiple loci. Proc. Natl. Acad. Sci. USA 98, 6709-6713
6. Fang, S., Takahashi, A., and Wu, C. -I. (2002) A mutation in the promoter of desaturase 2 is correlated with sexual isolation between Drosophila behavioral races. Genetics 162, 781-784
7. Kennison, J. A. (1981) The genetic and cytological organization of the Y chromosome of Drosophila Melanogaster. Genetics 98, 529-548
8. Gepner, J. and Hays, T. S. (1993) A fertility region on the Y chromosome of Drosophila melanogaster encodes a dynein microtubule motor. Proc. Natl. Acad. Sci. USA 90, 11132-11136
9. Hennig, W. (1993) Commentary| Conventional protein coding genes in the Drosophila Y chromosome: Is the puzzle of the fertility gene function solved? PNAS 90, 10904-40906
10. Reugels, A. M., Kurek, R., Lammerman, U., and Bunermann, H. (2000)Mega-introns in the dynein gene DhDhc7(Y) on the heterochromatic Y chromosome give rise to the giant threads loops in primary spermatocytes of Drosophila hydei. Genetics 154, 759-769
11. Carvalho, A. B., Lazzaro, B. P., and Clark, A. G. (2000) Y chromosomal fertility factors kl-2 and kl-3 of Drosophila melanogaster encode dynein heavy chain polypeptides. Proc. Natl. Acad. Sci. USA 97, 13239-13244
12. Carvalho, A. B., Dobo, B. A., Vibranovski, M. D., and Clark, A. G. (2001) Identification of five new genes on the Y chromosome of Drosophila melanogaster. Proc. Natl. Acad. Sci. USA 98, 13225-13230
13. Hong, G., Trumbly, R. J., Reimann, E. M., and Schlender, K. K. (2000)Sds22p is a subunit of a stable isolatable form of protein phosphatase 1 (Glc7p) from Saccharomyces cerevisiae. Arch. Biochem. Biophys. 376, 288-298
14. Kajava, A. V. (1998) Structural diversity of leucine-rich repeat proteins. J. Mol. Biol. 277, 519-527
15. Benashski, S. E., Patel-King, R. S. and Kingm S. M. (1999) Light chain 1 from the Chlamydomonas outer dynein arm is a leucine-rich repeat protein associated with the motor domain of the heavy chain. Biochemistry 38, 7253-7264
16. Lupas, A. (1996) Coiled coils: new structures and new functions. Trends Biochem. Sci. 21, 375-382
17. Hardy, R. W., Tokuyasu, K. T. and Lindsley, D. L. (1981) Analysis of spermatogenesis in Drosophila melanogaster bearing deletions for Y-chromosome fertility genes. Chromosoma 83, 593-617
15. Saitou, M., Furuse, M., Sasaki, H., Schulzke, J. D., Fromm, M., Takano, H., Noda, T., and Tsukita, S. (2000) Complex phenotype of mice lacking occludin, a component of tight junction strands. Mol. Biol. Cell 11, 4131-4142



